Sonikations-gestützte Proteinextraktion aus Tumorgewebe – Protokoll
Dieses Protokoll beschreibt eine sonikationsgestützte Proteinextraktionsmethode für Tumorgewebe, die den Standardarbeitsablauf der CPTAC-Harnstofflyse durch Hinzufügen eines kontrollierten Sondenbeschallungsschritts während des Gewebeaufbruchs erweitert. Aufbauend auf der etablierten CPTAC-Proteom- und Phosphoproteom-Präparationsstrategie verbessert diese Modifikation den Aufschluss von Zellen und subzellulären Strukturen, verringert die Probenviskosität und verbessert die Freisetzung von Proteinen, die mit der Harnstofflyse allein in der Regel schwieriger zu gewinnen sind, insbesondere membrangebundene und DNA-bindende oder kernassoziierte Proteine. In der zugrundeliegenden Studie erhöhte der sonikationsgestützte Arbeitsablauf die Erkennung sowohl von Proteinen als auch von Phosphopeptiden, während die Kompatibilität mit der nachgeschalteten CPTAC-ähnlichen Verdauung, TMT-Markierung, Fraktionierung, Phosphopeptidanreicherung und LC-MS/MS-Analysepipeline erhalten blieb.
Sonikationsunterstützte Proteinextraktion aus Tumorgewebe für die Tiefenproteom- und Phosphoproteomanalyse
 Das folgende Protokoll ist für die Extraktion von Proteinen aus kryopulverisiertem Tumorgewebe in 8 M Harnstoff-Lysepuffer optimiert: Ein zusätzlicher sondenartiger Beschallungsschritt verbessert die Gewinnung schwieriger Proteinklassen, insbesondere membranassoziierter und DNA-/Nukleus-assoziierter Proteine, vor dem Verdau und der anschließenden LC-MS/MS-Analyse. In der zugrundeliegenden Studie von Li et al. (2025) wurde durch die Hinzufügung der Beschallung die Erkennung von membran- und kernassoziierten Proteinen verbessert und eine tiefgreifende Abdeckung von >12.000 Proteinen und >25.000 Phosphopeptiden im Rahmen ihres Arbeitsablaufs unterstützt.
Das folgende Protokoll ist für die Extraktion von Proteinen aus kryopulverisiertem Tumorgewebe in 8 M Harnstoff-Lysepuffer optimiert: Ein zusätzlicher sondenartiger Beschallungsschritt verbessert die Gewinnung schwieriger Proteinklassen, insbesondere membranassoziierter und DNA-/Nukleus-assoziierter Proteine, vor dem Verdau und der anschließenden LC-MS/MS-Analyse. In der zugrundeliegenden Studie von Li et al. (2025) wurde durch die Hinzufügung der Beschallung die Erkennung von membran- und kernassoziierten Proteinen verbessert und eine tiefgreifende Abdeckung von >12.000 Proteinen und >25.000 Phosphopeptiden im Rahmen ihres Arbeitsablaufs unterstützt.

Ultraschallhomogenisator UP200St für die Proteinextraktion in der Proteomik
Anwendungsbereich des Protokolls
Verwenden Sie dieses Verfahren für:
- frisch gefrorenes, kryopulverisiertes Tumorgewebe
- Zellpellets oder andere biologische Proben, bei denen die Extraktion mit Harnstoff bereits etabliert ist
- globale Proteomik- und Phosphoproteomik-Workflows mit tryptischem Verdau und optionaler TMT-Markierung
In der Studie von Li et al. (2025) heißt es, dass der Arbeitsablauf auch auf andere Probentypen wie Zelllinien, Blut und Urin anwendbar ist, wobei jedoch je nach Probentyp eine Optimierung erforderlich sein kann.
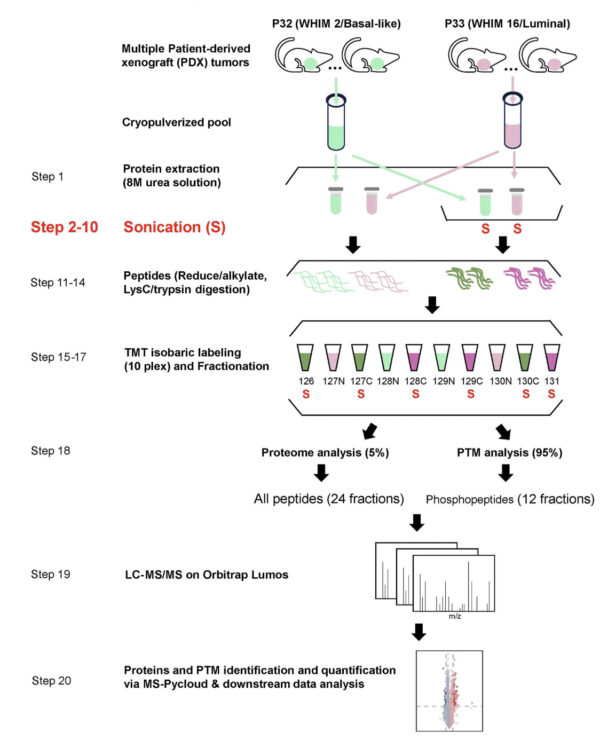
Optimierter Arbeitsablauf für die Probenvorbereitung mit implementiertem Sonikationsschritt. Der optimierte Arbeitsablauf und das experimentelle Design basieren auf dem CPTAC-Probenvorbereitungsprotokoll für globale proteomische und phosphoproteomische Analysen.
Studie und Schema: ©Li et al., 2025
Funktionsprinzip
In der ursprünglichen Studie wurde der standardmäßige CPTAC-Harnstoff-Lyse-Arbeitsablauf um die Beschallung erweitert und eine verbesserte Erkennung von Proteinen in Verbindung mit Membranen und Kernen festgestellt. Die Autoren stellen fest, dass die Beschallungsparameter in Bezug auf die Größe/Konzentration der Probe fein abgestimmt werden müssen – durch die Wahl der Sonotrodengröße, des Energieeintrags und der Impulszeit.
Exemplarisch für die Hielscher UP200Ht und UP200St bedeutet dies:
- Amplitude und Impulsmodus als Hauptsteuerungsgrößen verwenden
- die Proben durchgehend kühl halten (z. B. auf Eis)
- mit konservativen Einstellungen beginnen
- Optimierung in Bezug auf Probenklarheit, Temperatur, Proteinausbeute und nachgeschaltete Peptidqualität
Die beiden Hielscher 200-Watt-Schallgeräte UP200Ht und UP200St sind für kleine und mittlere Probenvolumina ausgelegt, mit einstellbaren Amplituden- und Impulseinstellungen; beide Ultraschallhomogenisatoren verfügen über eine digitale Touchscreen-Steuerung zur präzisen Parametereinstellung, automatische Datenaufzeichnung, steckbaren Temperatursensor, Fernbedienung, Probenbeleuchtung.
Reagenzien für die sonikationsunterstützte Proteinextraktion
Harnstoff-Lysepuffer
Unmittelbar vor der Verwendung frisch zubereiten:
- 8 M Harnstoff
- 75 mM NaCl
- 50 mM Tris, pH 8,0
- 1 mM EDTA
- 2 µg/mL Aprotinin
- 10 µg/mL Leupeptin
- 1 mM PMSF
- 10 mM NaF
- 20 µM PUGNAc
- Phosphatase-Inhibitor-Cocktail 2, 1:100 (v/v)
- Phosphatase-Inhibitor-Cocktail 3, 1:100 (v/v)
Harnstoff muss vor der Zugabe von Additiven vollständig aufgelöst sein; Inhibitoren sollten unmittelbar vor der Verwendung zugegeben werden; der Puffer sollte auf Eis gelagert werden; und nach der Zugabe von Additiven wird eher ein Schwenken als ein kräftiges Vortexen empfohlen.
Zusätzliche Reagenzien:
- BCA-Reagenzien für den Proteintest
- 50 mM Tris-HCl, pH 8,0
- DTT
- Iodacetamid
- LysC
- Trypsin
- Ameisensäure
- TMT-Reagenzien, falls quantitative Proteomik im Multiplexverfahren verwendet wird
- IMAC-Reagenzien, falls eine Phosphopeptidanreicherung durchgeführt wird

Ultraschallgerät UP200Ht mit Mikrotip S26d2 für die Probenvorbereitung
Ausrüstung für die sonikationsunterstützte Proteinextraktion
Erforderlich
Empfohlene Sondenauswahl
Für Proben im Bereich von 200-1000 µL sollten Sie eine Sonotrode mit kleinem Durchmesser verwenden, die für die direkte Bearbeitung kleiner Volumina mit hoher Intensität geeignet ist. Hielscher bietet mehrere Sonotroden-Durchmesser an, wobei kleinere Spitzendurchmesser eine höhere Intensität an der Spitze ermöglichen.
Praktischer Hinweis: Verwenden Sie die kleinste Sonde, die ein effizientes Mischen ohne übermäßige Schaumbildung oder Kontakt mit der Behälterwand ermöglicht.
Wenn Sie mit mehreren Proben gleichzeitig arbeiten, können Sie Folgendes in Betracht ziehen der Multi-Tube Sonicator VialTweeter oder der Mikroplatten-Sonicator UIP400MTP!
Schritt-für-Schritt-Anleitung: Verfahren der sonizitätsunterstützten Proteinextraktion
A. Vorkühlen und Vorbereiten
- Kühlen Sie die Zentrifuge auf 4°C ab.
- Bereiten Sie frischen Harnstoff-Lysepuffer vor und bewahren Sie ihn auf Eis auf.
- Stellen Sie die UP200Ht oder UP200St auf einem Ständer in einer Schallschutzkabine auf.
- Bereiten Sie ein Eisbad vor, das groß genug ist, um die Probenröhrchen aufrecht und stabil zu halten.
Die Zubereitung frischer Puffer und der Umgang mit Kälte sind entscheidend.
B. Initiale Harnstoffextraktion
- Bewahren Sie kryopulverisiertes Gewebe auf Eis auf.
- 200 µL gekühlten Harnstoff-Lysepuffer pro 50 mg feuchtes Gewebe hinzufügen.
- Wirbel 5-10 s bei hoher Geschwindigkeit.
- 15 Minuten bei 4°C inkubieren.
- Wiederholen Sie den Vortex-plus-Inkubationsschritt ein weiteres Mal.
- Bei 20.000 g für 10 Minuten bei 4°C zentrifugieren.
- Lysat/Supernatant in ein sauberes Röhrchen mit geringer Bindung überführen.
C. Beschallung mit UP200Ht oder UP200St
Ausgangsbedingungen für die Sonikation
- Amplitude: Beginn bei 20-30%
- Impulslänge: 5 s ON
- Kühlung: 2 Minuten auf Eis zwischen den Impulsen
- Anzahl der Zyklen: 4 Zyklen
- Gesamtdauer der aktiven Beschallung: 20 s
- Gesamtbearbeitungszeit einschließlich Kühlung: ca. 8-10 min
Schritte der Sonikation
- Überführen Sie das Lysat in ein für die Beschallung geeignetes Gefäß. Verwenden Sie ein schmales, dünnwandiges Gefäß, das einen guten Wärmeaustausch und ein sicheres Eintauchen der Sonde ermöglicht.
- Legen Sie das Röhrchen in ein Eisbad. In dem Papier wird die Kühlung während der Beschallung als entscheidend bezeichnet, um Hitzeschäden zu vermeiden.
- Tauchen Sie die Sondenspitze in die Probe ein. Halten Sie die Spitze für eine stabile Kavitation ausreichend eingetaucht, aber lassen Sie sie nicht die Rohrwand oder den Boden berühren.
- Führen Sie einen 5-Sekunden-Impuls mit der Startamplitude durch.
- Legen Sie die Probe sofort für 2 Minuten vollständig auf Eis.
- Wiederholen Sie den Vorgang, bis 4 Zyklen abgeschlossen sind.
- Überprüfen Sie das Lysat nach dem Zyklus.
- Fahren Sie nur bei Bedarf mit jeweils einem weiteren 5-Sekunden-Impuls fort, immer gefolgt von einer vollständigen Abkühlung.
- Stoppen Sie, sobald das Lysat gleichmäßiger und weniger faserig/viskos wird.
Der Endpunkt ist ein eher durchsichtiges Lysat, das eher Tropfen als einen kontinuierlichen viskosen Fluss bildet. - Zentrifugieren Sie bei etwa 16.000 g für 15 Minuten bei 4°C.
- Überführen Sie den geklärten Überstand in ein neues Röhrchen und messen Sie die Proteinkonzentration.
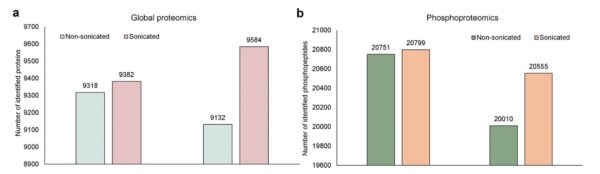
Vergleich der globalen Proteomik und Phosphoproteomik zwischen beschallten und nicht beschallten Proben.
a. Anzahl der identifizierten Proteine (globale Proteomik) in allen PDX-Tumorgeweben mit oder ohne Sonikation. b. Anzahl der identifizierten Phosphopeptide (IMAC-Anreicherung) in allen PDX-Tumorgeweben mit oder ohne Sonikation. Es wurden nur Proteine und Phosphopeptide gezählt, deren Abundanzverhältnis größer oder gleich dem 25. Das Abundanzverhältnis wurde zwischen denselben Probentypen berechnet.
Studie und Diagramme: ©Li et al., 2025
Nachgeschalteter Aufschluss und Analyse
Nach der Beschallung und Klärung verfahren Sie wie im ursprünglichen Arbeitsablauf nach CPTAC beschrieben:
- Lysat 1:3 (v/v) mit 50 mM Tris-HCl pH 8,0 verdünnen, um den Harnstoff auf <2 M.
- LysC in einer Menge von 1 mAU pro 50 µg Protein hinzufügen und 2 Stunden bei 25°C inkubieren.
- Trypsin im Verhältnis 1:49 Enzym:Substrat (w/w) zugeben und über Nacht bei 25°C verdauen.
- Abschrecken mit Ameisensäure auf 1% final.
- Weiter zu Entsalzung, TMT-Markierung, Fraktionierung, Phosphopeptidanreicherung und LC-MS/MS nach Bedarf.
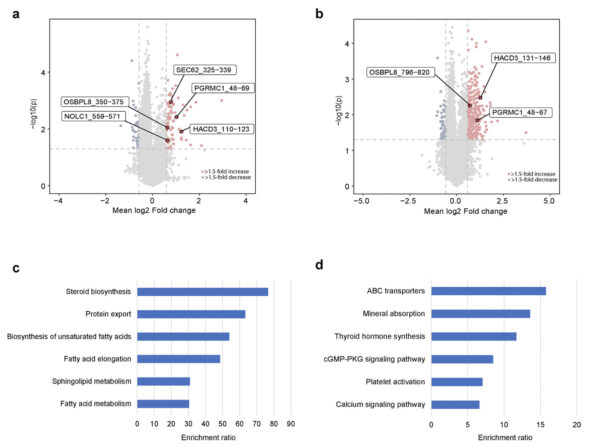
Unterschiedliche Expression von Phosphopeptiden aus TMT-markiertem MS.
a. Der basale Subtyp, Hervorhebung einiger menschlicher Phosphopeptide (Beginn und Ende der Proteinsequenz), die in beschallten Proben im Vergleich zu nicht beschallten Proben hochreguliert sind. b. Der luminale Subtyp, Hervorhebung einiger menschlicher Phosphopeptide (Beginn und Ende der Proteinsequenz), die in beschallten Proben im Vergleich zu nicht beschallten Proben hochreguliert sind. c. Angereicherte KEGG-Pfade auf der Grundlage der Proteine der hochregulierten Phosphopeptide im beschallten basalen Subtyp von Tumoren. d. Angereicherte KEGG-Pfade auf der Grundlage der Proteine der hochregulierten Phosphopeptide im beschallten luminalen Subtyp von Tumoren.
Studie und Diagramme: ©Li et al., 2025
Design, Herstellung und Beratung – Qualität Made in Germany
Hielscher Ultraschallgeräte sind bekannt für höchste Qualität und Designstandards. Robustheit und einfache Bedienung ermöglichen die problemlose Integration unserer Ultraschallgeräte in industrielle Anlagen. Raue Bedingungen und anspruchsvolle Umgebungen sind für Hielscher Ultraschallgeräte kein Problem.
Hielscher Ultrasonics ist ein ISO-zertifiziertes Unternehmen und legt großen Wert darauf, Hochleistungs-Ultraschallgeräte zu entwickeln und zu produzieren, die sich durch modernste Technik und Benutzerfreundlichkeit auszeichnen. Selbstverständlich sind Hielscher Sonicators CE-konform und erfüllen die Anforderungen von UL, CSA und RoHs.

Multiwell-Platten-Sonicator UIP400MTP für die Proteinextraktion aus Proben im Hochdurchsatzverfahren
Literatur / Literaturhinweise
- Li Q.K.; Lih T.M.; Clark D.J.; Chen L.; Schnaubelt M.; Zhang H. (2025): Sonication-assisted protein extraction improves proteomic detection of membrane-bound and DNA-binding proteins from tumor tissues. Nature Protocols 2025 Aug;20(8):2083-2099.
- Stadlmann, J., Taubenschmid, J., Wenzel, D. et al. (2017): Comparative glycoproteomics of stem cells identifies new players in ricin toxicity. Nature 549, 2017. 538–542
- Jakob, S., Steinchen, W., Hanßmann, J. et al. (2024): The virulence regulator VirB from Shigella flexneri uses a CTP-dependent switch mechanism to activate gene expression. Nature Communications 15, 318 (2024).
- Jorge S., Capelo J.L., LaFramboise W., Dhir R., Lodeiro C., Santos H.M. (2019): Development of a Robust Ultrasonic-Based Sample Treatment To Unravel the Proteome of OCT-Embedded Solid Tumor Biopsies. Journal of Proteome Research 2019 Jul 5;18(7):2979-2986.
- Mertins P, Tang LC, Krug K, et al. (2018): Reproducible workflow for multiplexed deep-scale proteome and phosphoproteome analysis of tumor tissues by liquid chromatography-mass spectrometry. (Initial CPTAC protocol). Nature Protocols 7, 2018. 1632-1661.
Häufig gestellte Fragen
Was ist der Unterschied zwischen der Proteinextraktion aus Pflanzengewebe und aus Säugetiergewebe?
Die Proteinextraktion aus Pflanzengewebe ist in der Regel schwieriger als aus Säugetiergewebe, da Pflanzenzellen eine starre, zellulosereiche Zellwand, reichlich Polysaccharide, phenolische Verbindungen, Pigmente und aktive endogene Enzyme aufweisen, die die Proteinsolubilisierung beeinträchtigen, die Extrakte verunreinigen oder den Proteinabbau fördern können. Im Gegensatz dazu hat Säugetiergewebe keine Zellwand und lässt sich im Allgemeinen leichter chemisch aufbrechen, obwohl es oft mehr Lipide, extrazelluläre Matrix und Proteasen enthält, die die Extraktion erschweren können. Daher erfordern Pflanzenprotokolle in der Regel einen stärkeren mechanischen Aufschluss, eine Zerkleinerung bei niedrigen Temperaturen und Zusätze wie PVPP, Reduktionsmittel oder Reinigungsmittel auf Phenolbasis, während Säugetiergewebe häufiger erfolgreich mit Puffern auf Detergensbasis wie RIPA oder harnstoffbasierten Lysesystemen behandelt wird. Sowohl Pflanzen- als auch Säugetiergewebe kann durch Sonikation effizient lysiert werden!
Wie kann die Proteinextraktion aus Gewebe mit RIPA-Puffer verbessert werden?
Die Proteinextraktion aus Gewebe mit RIPA-Puffer kann verbessert werden, indem sowohl der Aufschluss als auch der Schutz der Probe optimiert werden. Die wichtigsten Maßnahmen bestehen darin, das Gewebe und den Puffer kalt zu halten, frisch zubereitete Protease- und Phosphataseinhibitoren zu verwenden, das Gewebe vor der Lyse gründlich zu zerkleinern oder zu pulverisieren, ein angemessenes Verhältnis von Puffer zu Gewebe beizubehalten und einen mechanischen Aufschlussschritt wie Homogenisierung oder kurze Sondenbeschallung hinzuzufügen, um dichtes Gewebe aufzubrechen und die Viskosität zu verringern. Die Extraktionseffizienz verbessert sich auch, wenn die Lysate auf Eis bebrütet und intermittierend gemischt werden, gefolgt von einer gekühlten Hochgeschwindigkeitszentrifugation zur Entfernung unlöslicher Trümmer. Bei faserigem, lipidreichem oder stark strukturiertem Gewebe kann eine einmalige Wiederholung der Extraktion oder eine längere Einwirkzeit des Detergens die Gewinnung verbessern, doch sollte eine übermäßige Beschallung oder eine längere Behandlung bei Raumtemperatur vermieden werden, da sie Proteine denaturieren oder die Proteolyse verstärken können.
Welche Sicherheitsanforderungen sollten bei der Proteinextraktion mit Ultraschall beachtet werden?
Führen Sie die Sondenbeschallung in einer Schallschutzbox oder mit geeignetem Gehörschutz durch. Im Quellenprotokoll wird ausdrücklich vor schädlichen akustischen Geräuschen gewarnt, die während der Beschallung entstehen.
Tragen Sie einen Augenschutz, einen Laborkittel und Handschuhe.
Halten Sie die Sonde von der Haut fern und beschallen Sie niemals ein offenes Gefäß ohne Spritzschutz.
Handhaben Sie PMSF und andere Inhibitoren gemäß den örtlichen Vorschriften zur Chemikaliensicherheit.
Bewahren Sie die Proben auf Eis auf, um hitzebedingte Proteinschäden zu vermeiden; in dem Papier wird die Temperaturkontrolle wiederholt als entscheidend bezeichnet.

Der VialTweeter Sonicator beschleunigt und verbessert die Proteinextraktion in der Proteomik

Hielscher Ultrasonics fertigt Hochleistungs-Ultraschall-Homogenisatoren vom Labor bis zum voll-kommerziellen Industriemaßstab.


