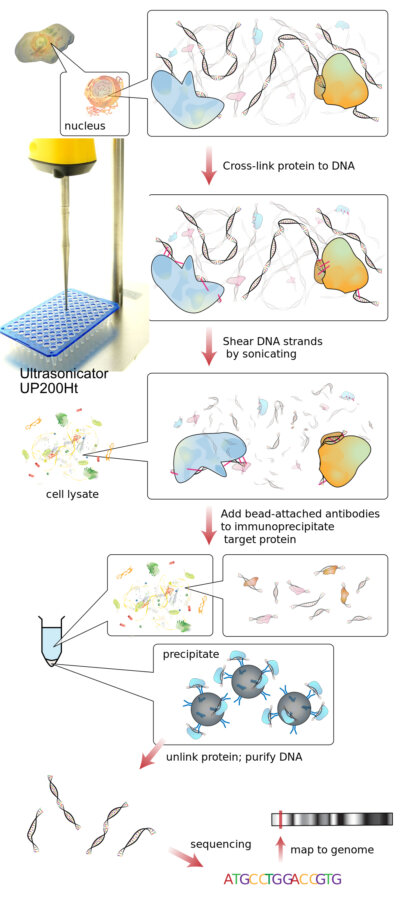
Scherung von Chromatin mit Sonikation
Das Scheren von Chromatin ist ein entscheidender Schritt in vielen epigenetischen und molekularbiologischen Arbeitsabläufen, insbesondere bei der Chromatin-Immunpräzipitation (ChIP), ChIP-seq und verwandten Assays. Ziel ist es, Chromatin in reproduzierbare DNA-Protein-Komplexe zu fragmentieren und dabei die Epitopintegrität zu erhalten und den Probenverlust zu minimieren. Unter den verfügbaren Methoden hat sich die Chromatinfragmentierung mit Ultraschall zu einem weit verbreiteten Ansatz entwickelt, da sie eine zuverlässige, reagenzienfreie Fragmentierung mit hervorragender Reproduzierbarkeit ermöglicht.
Was sollte ich beim Scheren von Chromatin beachten?
Effizientes Chromatin-Shearing erfordert eine sorgfältige Kontrolle der Versuchsparameter. Eine unsachgemäße Fragmentierung kann nachgelagerte ChIP-Experimente beeinträchtigen, indem sie Fragmente erzeugt, die entweder zu groß, zu stark abgebaut oder zwischen den Proben inkonsistent sind.
Einer der wichtigsten Faktoren ist die gewünschte Fragmentgrößenverteilung. Für die meisten ChIP- und ChIP-seq-Anwendungen sind Chromatinfragmente zwischen 100 und 600 Basenpaaren optimal. Dieser Größenbereich ermöglicht eine effiziente Immunpräzipitation und bietet gleichzeitig eine ausreichende Auflösung für die genomische Kartierung.
 Ein weiterer Schlüsselfaktor ist die Vernetzungseffizienz vor der Sonikation. Die meisten ChIP-Arbeitsabläufe beinhalten eine Fixierung mit Formaldehyd, um Protein-DNA-Wechselwirkungen zu stabilisieren. Eine übermäßige Vernetzung kann das Chromatin jedoch widerstandsfähiger gegen eine Fragmentierung machen, so dass längere Beschallungszeiten erforderlich sind und die Wärmebelastung möglicherweise zunimmt.
Ein weiterer Schlüsselfaktor ist die Vernetzungseffizienz vor der Sonikation. Die meisten ChIP-Arbeitsabläufe beinhalten eine Fixierung mit Formaldehyd, um Protein-DNA-Wechselwirkungen zu stabilisieren. Eine übermäßige Vernetzung kann das Chromatin jedoch widerstandsfähiger gegen eine Fragmentierung machen, so dass längere Beschallungszeiten erforderlich sind und die Wärmebelastung möglicherweise zunimmt.
Auch die Temperaturkontrolle ist entscheidend. Bei der Sonikation wird örtlich begrenzte Energie erzeugt, die die Probentemperatur erhöhen kann. Erhöhte Temperaturen können die DNA schädigen oder Proteine denaturieren, was die Erkennung von Antikörpern bei ChIP beeinträchtigt. Viele Forscher führen daher gepulste Beschallungszyklen in Kombination mit Kühlintervallen durch, um die Probenstabilität zu erhalten.
Probenkonzentration und -volumen beeinflussen ebenfalls die Fragmentierungseffizienz. Hochkonzentrierte Chromatinsuspensionen können längere Beschallungszeiten erfordern, während kleine Probenvolumina eine präzise Energiezufuhr erfordern, um eine Überbearbeitung zu vermeiden.
Schließlich hat auch die Wahl des Beschallungsgeräts großen Einfluss auf die Reproduzierbarkeit der Versuche. Geräte, die für das Scheren von Chromatin entwickelt wurden, bieten in der Regel eine kontrollierte Ultraschallenergie und eine standardisierte Probenhandhabung, die eine einheitliche Fragmentierung über mehrere Proben hinweg ermöglicht.
Welchen Sonicator sollte ich für das Chromatin-Shearing wählen?
Verschiedene Laborarbeitsabläufe erfordern unterschiedliche Beschallungskonfigurationen. Das optimale System hängt weitgehend vom Probendurchsatz, dem Volumen und dem Versuchsformat ab.
Sondensonicator-Typ
Ein Sondensonicator gibt Ultraschallenergie über eine Titansonde direkt in die Probe ab. Diese Konfiguration bietet eine sehr hohe Energiedichte und eignet sich daher für eine robuste Chromatindisruption in einzelnen Proben.
Sonotroden sind besonders nützlich für:
- Kleine bis mittelgroße Stichprobenzahlen
- Schwierig zu fragmentierendes Chromatin
- Flexible Versuchsprotokolle
Mehrröhriger Sonicator - VialTweeter
Für Laboratorien, die mehrere Proben gleichzeitig bearbeiten, bietet der VialTweeter-Multitube-Sonicator eine äußerst reproduzierbare Lösung. Das System überträgt die Ultraschallenergie indirekt durch den Röhrchenhalter, so dass mehrere versiegelte Röhrchen unter identischen Bedingungen fragmentiert werden können.
Diese Konfiguration bietet wichtige Vorteile:
- Paralleles Scheren von Chromatin aus mehreren Proben
- Beseitigung der Sondenkontamination
- Hohe Reproduzierbarkeit zwischen Röhrchen
- Vereinfachter Arbeitsablauf für die Vorbereitung von ChIP-Proben
Solche Mehrröhrensysteme eignen sich gut für routinemäßige ChIP-Experimente und Studien mit mittlerem Durchsatz.
Mikroplatten-Sonicator - UIP400MTP
Epigenetikstudien mit hohem Durchsatz stützen sich zunehmend auf eine mikroplattenbasierte Probenverarbeitung. Der Mikroplatten-Sonicator UIP400MTP wurde entwickelt, um Chromatin direkt in Standard-Mikroplatten zu fragmentieren, ohne Proben zu transferieren.
Dieser Ansatz ermöglicht:
- Gleichzeitige Verarbeitung von Dutzenden oder Hunderten von Proben
- Automatisierungsfreundliche Arbeitsabläufe
- Gleichmäßige Verteilung der Ultraschallenergie über die Bohrlöcher
- Signifikante Reduzierung der Probenhandhabungsschritte
Für große ChIP-seq-Screening-Projekte oder epigenetische Hochdurchsatzstudien bietet die Mikroplattenbeschallung außergewöhnliche Skalierbarkeit und Effizienz. Der Multi-Well-Platten-Sonicator UIP400MTP ist gut geeignet für Integration in Liquid-Handling-Systeme und automatisierte Laborabläufe.
Warum sollte man sich für die Sonikation und nicht für andere Techniken der Chromatinscherung entscheiden?
Im Vergleich zu enzymatischen Ansätzen bietet die Beschallung für ChIP eine unvoreingenommene Fragmentierung, da der Prozess nicht von sequenzspezifischer Enzymaktivität abhängt. Dies ist besonders wichtig für genomweite epigenetische Studien, bei denen eine einheitliche Abdeckung unerlässlich ist.
Ein weiterer großer Vorteil ist die Skalierbarkeit. Ultraschallsysteme können einzelne Proben, mehrere Röhrchen oder ganze Mikrotiterplatten aufnehmen, so dass die Labors die für ihren experimentellen Durchsatz am besten geeignete Konfiguration wählen können.
Schließlich bietet die Beschallung eine hervorragende Kontrolle über die Fragmentierungsparameter. Durch die Anpassung von Impulszyklen, Dauer und Leistung können Forscher zuverlässig die gewünschte Fragmentgrößenverteilung erreichen.
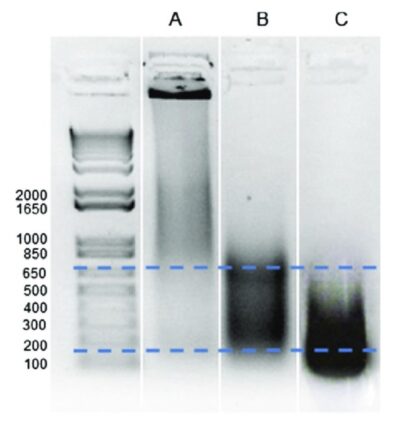
Chromatinfragmentierung durch optimierte Sonikation von ChIP-Proben.
(a) keine Scherung (lange Fragmente im Gel);
(b) optimales Fragmentierungsprofil (Anreicherung von Fragmenten mit 200-600 bp);
(c) übermäßige DNA-Fragmentierung (Überrepräsentation von Fragmenten, die kürzer als 200 bp sind)
Jarillo et al. (2018)
Vergleich von Chromatin-Shearing-Techniken
| Methode der Chromatinscherung | Grundsatz | Vorteile | Beschränkungen |
| Beschallung | Hochfrequente akustische Energie fragmentiert mechanisch das Chromatin. | Reagenzienfreie Fragmentierung, hochgradig reproduzierbare Ergebnisse, abstimmbare Fragmentgrößenverteilung, kompatibel mit quervernetztem Chromatin, skalierbar von Einzelröhrchen bis zu Mehrfachproben und Mikroplattenformaten. | Erfordert eine Beschallungsanlage und die Optimierung der Beschallungsparameter. |
| Enzymatische Verdauung (MNase) | Die mikrokokkale Nuklease verdaut die DNA zwischen den Nukleosomen. | Sanfte Fragmentierung und nützlich für die Analyse von nativem Chromatin. | Enzymverzerrung, Sequenzpräferenz, schwer zu kontrollierender Verdau, potenzielle Variabilität zwischen Experimenten. |
| Mechanische Scherung (Nadel/Spritze) | Das Chromatin wird durch wiederholte physische Krafteinwirkung aufgebrochen. | Einfache Methode, die nur wenig Ausrüstung erfordert. | Schlechte Reproduzierbarkeit, begrenzte Kontrolle über die Fragmentgröße, arbeitsintensiv bei mehreren Proben. |
| Vernebelung | Die Druckluft drückt die DNA durch kleine Öffnungen und verursacht eine Fragmentierung. | Schneller Fragmentierungsprozess. | Möglicher Probenverlust, begrenzte Skalierbarkeit, erfordert spezielle Ausrüstung. |
Wie kann ich die Chromatinausbeute nach der Ultraschallfragmentierung quantifizieren und qualifizieren?
 Nach der Beschallung für ChIP müssen die Forscher sowohl die Quantität als auch die Qualität des fragmentierten Chromatins bewerten. Dieser Überprüfungsschritt stellt sicher, dass die Chromatinfragmentierung den Anforderungen nachgelagerter Anwendungen wie ChIP-qPCR oder ChIP-seq entspricht.
Nach der Beschallung für ChIP müssen die Forscher sowohl die Quantität als auch die Qualität des fragmentierten Chromatins bewerten. Dieser Überprüfungsschritt stellt sicher, dass die Chromatinfragmentierung den Anforderungen nachgelagerter Anwendungen wie ChIP-qPCR oder ChIP-seq entspricht.
Die Quantifizierung beginnt in der Regel mit der Messung der DNA-Konzentration. Spektrophotometrische Methoden wie die Nanodrop-Analyse oder fluorometrische Assays wie die Qubit-DNA-Quantifizierung liefern zuverlässige Schätzungen der Chromatinausbeute nach der Devernetzung und Aufreinigung.
Die DNA-Konzentration allein sagt jedoch nichts darüber aus, ob die Fragmentierung erfolgreich war. Daher bewerten die Forscher die Größenverteilung der Fragmente mithilfe elektrophoretischer Techniken. Die Agarosegel-Elektrophorese ist nach wie vor ein gängiges Verfahren, um DNA-Fragmente sichtbar zu machen und zu überprüfen, ob die meisten in den angestrebten Größenbereich fallen.
Fortgeschrittene Labors verwenden häufig Kapillarelektrophorese-Systeme wie den Agilent Bioanalyzer oder die TapeStation. Diese Plattformen liefern präzise Größenverteilungsprofile und ermöglichen es den Forschern, eine übermäßige Fragmentierung oder unvollständige Scherung zu erkennen.
Bei der Bewertung der Chromatinqualität nach der Ultraschallfragmentierung bestätigen die Forscher in der Regel:
- Die meisten DNA-Fragmente liegen im Bereich von 100-600 bp
- Die Verteilung der Fragmente ist bei allen Wiederholungsproben gleich.
- Der DNA-Abbau ist minimal
- Die Gesamtchromatinausbeute reicht für den geplanten ChIP-Assay aus.
Eine ordnungsgemäße Qualitätskontrolle gewährleistet, dass die Ultraschall-Chromatinschere reproduzierbare und biologisch aussagekräftige Ergebnisse liefert.
Schlussfolgerung: Ultraschall-Chromatin-Scherung für zuverlässige Forschung
Ein zuverlässiges Scheren von Chromatin ist für eine erfolgreiche ChIP- und Epigenetik-Forschung unerlässlich. Die Ultraschallfragmentierung bietet eine leistungsstarke Lösung, da sie einen präzisen, reproduzierbaren und reagenzienfreien Aufschluss von Chromatin in einer Vielzahl von Versuchsformaten ermöglicht.
Durch sorgfältige Optimierung der Beschallungsparameter, Überprüfung der Fragmentgrößenverteilung und Auswahl des geeigneten Beschallungssystems – ob ein Sondenschallkopf, ein VialTweeter mit mehreren Rohren oder der Mikroplattenschallkopf UIP400MTP mit hohem Durchsatz – können Forscher eine konsistente Chromatinfragmentierung erreichen, die hochwertige ChIP- und ChIP-seq-Ergebnisse unterstützt.
Da die Epigenetik-Forschung immer mehr auf einen höheren Durchsatz und eine bessere Reproduzierbarkeit der Experimente abzielt, ist die Ultraschall-Chromatinscherung nach wie vor eine der vielseitigsten und zuverlässigsten Methoden für moderne molekularbiologische Labors.
Design, Herstellung und Beratung – Qualität Made in Germany
Hielscher Ultraschallgeräte sind bekannt für höchste Qualität und Designstandards. Robustheit und einfache Bedienung ermöglichen die problemlose Integration unserer Ultraschallgeräte in industrielle Anlagen. Raue Bedingungen und anspruchsvolle Umgebungen sind für Hielscher Ultraschallgeräte kein Problem.
Hielscher Ultrasonics ist ein ISO-zertifiziertes Unternehmen und legt großen Wert darauf, Hochleistungs-Ultraschallgeräte zu entwickeln und zu produzieren, die sich durch modernste Technik und Benutzerfreundlichkeit auszeichnen. Selbstverständlich sind Hielscher Sonicators CE-konform und erfüllen die Anforderungen von UL, CSA und RoHs.
Literatur / Literaturhinweise
- Dreyer J., Ricci G., van den Berg J., Bhardwaj V., Funk J., Armstrong C., van Batenburg V., Sine C., VanInsberghe M.A., Marsman R., Mandemaker I.K., di Sanzo S., Costantini J., Manzo S.G., Biran A., Burny C., Völker-Albert M., Groth A., Spencer S.L., van Oudenaarden A., Mattiroli F. (2024): Acute multi-level response to defective de novo chromatin assembly in S-phase. Molecular Cell 2024.
- Mittal, N., Guimaraes, J.C., Gross, T. et al. (2017): The Gcn4 transcription factor reduces protein synthesis capacity and extends yeast lifespan. Nat Commun 8, 457 (2017).
- Shih H.-T., Chen W.-Y., Liu K.-Y., Shih Z.-S., Chen Y.-J., Hsieh P.-C., et al. (2016): dBRWD3 Regulates Tissue Overgrowth and Ectopic Gene Expression Caused by Polycomb Group Mutations. PLoS Genetics 12(9): e1006262.
- José A. Jarillo, Dorota N. Komar, and Manuel Piñeiro (2018): The Use of the Chromatin Immunoprecipitation Technique for In Vivo Identification of Plant Protein–DNA Interactions. Chapter in book: Luis Oñate-Sánchez (ed.), Two-Hybrid Systems: Methods and Protocols, Methods in Molecular Biology, vol. 1794, 2018.
- Einig, E., Jin, C., Andrioletti, V. et al. (2023): RNAPII-dependent ATM signaling at collisions with replication forks. Nature Communications 14, 5147 (2023)
Häufig gestellte Fragen
Was ist Chromatin?
Chromatin ist der Strukturkomplex aus DNA und zugehörigen Proteinen, der das genetische Material im Zellkern eukaryontischer Zellen organisiert. Die wichtigsten Proteine im Chromatin sind Histone, um die die DNA zu Nukleosomen gewickelt ist. Diese Organisation verdichtet die DNA und regelt gleichzeitig den Zugang zur genetischen Information für Prozesse wie Transkription, Replikation und DNA-Reparatur.
Welche Arten von Chromatin gibt es?
Chromatin wird im Allgemeinen in zwei Hauptformen unterteilt: Euchromatin und Heterochromatin. Euchromatin ist locker gepackt und transkriptionell aktiv, so dass die Gene für die Transkriptionsmaschinerie leicht zugänglich sind. Heterochromatin ist dichter gepackt und transkriptionell inaktiv und enthält typischerweise repetitive DNA-Sequenzen oder Gene, die zum Schweigen gebracht wurden. Heterochromatin kann weiter unterteilt werden in konstitutives Heterochromatin, das permanent kondensiert bleibt, und fakultatives Heterochromatin, das je nach den zellulären Bedingungen zwischen aktivem und inaktivem Zustand wechseln kann.
Was ist Crosslinking?
Vernetzung ist ein biochemischer Prozess, der zur Stabilisierung von Wechselwirkungen zwischen Biomolekülen durch die Bildung kovalenter Bindungen zwischen ihnen eingesetzt wird. In der Chromatinforschung wird die Vernetzung üblicherweise eingesetzt, um Protein-DNA-Wechselwirkungen innerhalb des Chromatins vor der Analyse zu erhalten. Chemische Stoffe wie Formaldehyd werden in der Regel verwendet, um reversible kovalente Bindungen zwischen DNA und assoziierten Proteinen zu schaffen, die effektiv „Gefrieren“ molekulare Interaktionen zu einem bestimmten Zeitpunkt. Durch diese Stabilisierung können Chromatinkomplexe fragmentiert und verarbeitet werden, ohne dass die nativen Verbindungen zwischen DNA und regulatorischen Proteinen verloren gehen, was für Techniken wie die Chromatin-Immunpräzipitation (ChIP) unerlässlich ist.
Was ist ChIP?
Die Chromatin-Immunpräzipitation (ChIP) ist ein molekularbiologisches Verfahren zur Untersuchung von Wechselwirkungen zwischen Proteinen und DNA im Chromatin. Bei dieser Methode werden die DNA-Protein-Komplexe zunächst stabilisiert, in der Regel durch Quervernetzung, und das Chromatin wird dann fragmentiert. Mit Hilfe von Antikörpern, die für ein Zielprotein spezifisch sind, werden die Protein-DNA-Komplexe immunpräzipitiert, so dass die zugehörigen DNA-Sequenzen isoliert und analysiert werden können.
Wofür wird ChIP verwendet?
ChIP wird eingesetzt, um Genomregionen zu identifizieren, die von bestimmten DNA-assoziierten Proteinen wie Transkriptionsfaktoren, Histonmodifikationen oder Chromatin-assoziierten regulatorischen Proteinen gebunden werden. Diese Technik wird häufig zur Untersuchung der Genregulation, epigenetischer Veränderungen, der Bindungsstellen von Transkriptionsfaktoren und der Chromatinstruktur eingesetzt. In Kombination mit nachgeschalteten Analysemethoden wie der quantitativen PCR (ChIP-qPCR) oder der Hochdurchsatzsequenzierung (ChIP-seq) ermöglicht sie die genomweite Kartierung von Protein-DNA-Interaktionen.
Welche Arten von ChIP gibt es?
Es gibt mehrere Varianten der Chromatin-Immunpräzipitation, die von der Versuchsplanung und der nachgeschalteten Analyse abhängen. Zu den gebräuchlichsten Ansätzen gehören die ChIP-qPCR, bei der die Anreicherung spezifischer Genomregionen quantifiziert wird, die ChIP-seq, bei der Next-Generation-Sequenzierung zur Kartierung von Protein-DNA-Interaktionen im gesamten Genom eingesetzt wird, und der ChIP-Chip, bei dem die ChIP mit der DNA-Mikroarray-Analyse kombiniert wird. Weitere Varianten wie die native ChIP (N-ChIP), bei der nicht vernetztes Chromatin analysiert wird, und die vernetzte ChIP (X-ChIP), bei der chemische Vernetzungen zur Stabilisierung von Protein-DNA-Wechselwirkungen eingesetzt werden, sind je nach der zu untersuchenden biologischen Fragestellung ebenfalls weit verbreitet.

Hielscher Ultrasonics fertigt Hochleistungs-Ultraschall-Homogenisatoren vom Labor bis zum voll-kommerziellen Industriemaßstab.