Estrazione di proteine da tessuto tumorale assistita da sonicazione – protocollo
Questo protocollo descrive un metodo di estrazione proteica assistita da sonicazione per il tessuto tumorale che migliora il flusso di lavoro standard della lisi ureica CPTAC aggiungendo una fase di sonicazione controllata della sonda durante la disgregazione del tessuto. Basandosi sulla consolidata strategia di preparazione del proteoma e del fosfoproteoma su scala profonda CPTAC, questa modifica migliora la disgregazione delle cellule e della struttura subcellulare, riduce la viscosità del campione e aumenta il rilascio di proteine che in genere sono più difficili da recuperare con la sola lisi ureica, in particolare le proteine legate alla membrana e quelle legate al DNA o associate al nucleo. Nello studio sottostante, il flusso di lavoro assistito dalla sonicazione ha aumentato il rilevamento di proteine e fosfopeptidi, preservando la compatibilità con la digestione in stile CPTAC, l'etichettatura TMT, il frazionamento, l'arricchimento dei fosfopeptidi e la pipeline di analisi LC-MS/MS.
Estrazione di proteine da tessuto tumorale assistita da sonicazione per l'analisi proteomica e fosfoproteomica profonda
 Il seguente protocollo è ottimizzato per l'estrazione di proteine da tessuto tumorale criopolverizzato in tampone di lisi 8 M urea: L'aggiunta di una fase di sonicazione di tipo sonda migliora il recupero di classi proteiche difficili, in particolare le proteine associate alla membrana e al DNA/nucleo, prima della digestione e dell'analisi LC-MS/MS a valle. Nello studio di base di Li et al. (2025), l'aggiunta della sonicazione ha aumentato il rilevamento delle proteine associate alla membrana e al nucleo e ha supportato la copertura su scala profonda di >12.000 proteine e >25.000 fosfopeptidi nel loro flusso di lavoro.
Il seguente protocollo è ottimizzato per l'estrazione di proteine da tessuto tumorale criopolverizzato in tampone di lisi 8 M urea: L'aggiunta di una fase di sonicazione di tipo sonda migliora il recupero di classi proteiche difficili, in particolare le proteine associate alla membrana e al DNA/nucleo, prima della digestione e dell'analisi LC-MS/MS a valle. Nello studio di base di Li et al. (2025), l'aggiunta della sonicazione ha aumentato il rilevamento delle proteine associate alla membrana e al nucleo e ha supportato la copertura su scala profonda di >12.000 proteine e >25.000 fosfopeptidi nel loro flusso di lavoro.

Sonda a ultrasuoni UP200St per l'estrazione delle proteine in proteomica
Area di applicazione del protocollo
Utilizzare questa procedura per:
- tessuto tumorale fresco congelato e criopolverizzato
- pellet di cellule o altri campioni biologici in cui l'estrazione a base di urea è già stata stabilita
- flussi di lavoro di proteomica globale e fosfoproteomica che utilizzano la digestione triptica e l'etichettatura TMT opzionale
Lo studio di Li et al. (2025) afferma che il flusso di lavoro è applicabile anche ad altri tipi di campioni, come linee cellulari, sangue e urine, ma potrebbe essere necessaria un'ottimizzazione in base al tipo di campione.
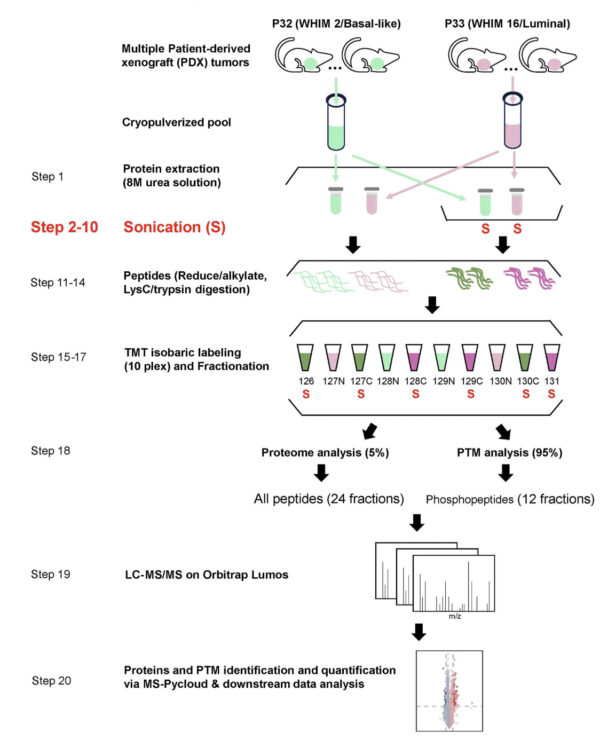
Flusso di lavoro ottimizzato per la preparazione dei campioni con implementazione della fase di sonicazione. Il flusso di lavoro ottimizzato e il disegno sperimentale si basano sul protocollo di preparazione dei campioni CPTAC per l'analisi proteomica e fosfoproteomica globale.
Studio e schema: ©Li et al., 2025
Principio di funzionamento
Lo studio originale ha aggiunto la sonicazione al flusso di lavoro standard di lisi dell'urea CPTAC e ha rilevato un miglioramento nella rilevazione delle proteine associate alle membrane e ai nuclei. Gli autori affermano che i parametri di sonicazione devono essere regolati con precisione in base alle dimensioni/concentrazione del campione. – scegliendo le dimensioni del sonotrodo, l'energia immessa e la tempistica degli impulsi.
Ad esempio, per gli Hielscher UP200Ht e UP200St, ciò significa:
- utilizzare l'ampiezza e la modalità di impulso come variabili di controllo principali
- mantenere i campioni al freddo (ad esempio, nel ghiaccio)
- iniziare con impostazioni conservative
- ottimizzare rispetto alla limpidezza del campione, alla temperatura, alla resa proteica e alla qualità dei peptidi a valle
Entrambi i sonicatori Hielscher da 200 watt UP200Ht e UP200St sono progettati per volumi di campione piccoli e medi, con impostazioni di ampiezza e impulso regolabili; entrambi gli omogeneizzatori a ultrasuoni sono dotati di controllo digitale touchscreen per la regolazione precisa dei parametri, registrazione automatica dei dati, sensore di temperatura collegabile, controllo remoto, illuminazione del campione.
Reagenti per l'estrazione di proteine assistita da sonicazione
Tampone di lisi con urea
Preparare il prodotto fresco immediatamente prima dell'uso:
- 8 M urea
- 75 mM NaCl
- 50 mM Tris, pH 8,0
- 1 mM EDTA
- 2 µg/mL di aprotinina
- 10 µg/mL leupeptina
- 1 mM PMSF
- 10 mM NaF
- 20 µM PUGNAc
- Cocktail di inibitori della fosfatasi 2, 1:100 (v/v)
- Cocktail di inibitori della fosfatasi 3, 1:100 (v/v)
L'urea deve essere completamente disciolta prima di aggiungere gli additivi; gli inibitori devono essere aggiunti immediatamente prima dell'uso; il tampone deve essere conservato in ghiaccio; dopo l'aggiunta degli additivi si raccomanda di agitare piuttosto che agitare vigorosamente.
Reagenti aggiuntivi:
- Reagenti per il dosaggio delle proteine BCA
- 50 mM Tris-HCl, pH 8,0
- DTT
- Iodoacetamide
- LysC
- tripsina
- Acido formico
- Reagenti TMT, se si utilizza la proteomica quantitativa multiplexed
- reagenti IMAC, se si esegue l'arricchimento dei fosfopeptidi

Ultrasuonatore UP200Ht con micropunte S26d2 per la preparazione del campione
Apparecchiatura per l'estrazione di proteine assistita da sonicazione
Richiesto
Selezione della sonda consigliata
Per campioni di circa 200-1000 µL, utilizzare un sonotrodo di piccolo diametro adatto all'elaborazione diretta ad alta intensità di piccoli volumi. Hielscher offre diversi diametri di sonotrodi e i diametri più piccoli delle punte garantiscono un'intensità maggiore sulla punta.
Nota pratica: utilizzare la sonda più piccola per ottenere una miscelazione efficace senza eccessiva formazione di schiuma o contatto con le pareti del recipiente.
Se si lavora con più campioni contemporaneamente, è possibile considerare il Sonicator multi-tubo VialTweeter o il Sonicatore per micropiastre UIP400MTP!
Istruzioni passo-passo: Procedura di estrazione delle proteine assistita da sonicazione
A. Preraffreddamento e preparazione
- Raffreddare la centrifuga a 4°C.
- Preparare un tampone di lisi di urea fresco e tenerlo in ghiaccio.
- Installare l'UP200Ht o l'UP200St su un supporto all'interno di una cassa acustica.
- Preparare un bagno di ghiaccio sufficientemente grande da tenere le provette di campione in posizione verticale e stabile.
La preparazione del tampone fresco e la manipolazione a freddo sono fondamentali.
B. Estrazione iniziale dell'urea
- Conservare il tessuto criopolverizzato nel ghiaccio.
- Aggiungere 200 µL di tampone di lisi ureico raffreddato per 50 mg di tessuto umido.
- Vortex 5-10 s ad alta velocità.
- Incubare 15 minuti a 4°C.
- Ripetere ancora una volta la fase di vortex e di incubazione.
- Centrifugare a 20.000g per 10 minuti a 4°C.
- Trasferire il lisato/supernatante in una provetta pulita a basso legame.
C. Sonicazione con UP200Ht o UP200St
Condizioni di partenza per la sonicazione
- Ampiezza: iniziare con il 20-30%.
- Durata dell'impulso: 5 s ON
- Raffreddamento: 2 minuti con ghiaccio tra gli impulsi
- Numero di cicli: 4 cicli
- Tempo totale di sonicazione attiva: 20 s
- Tempo totale di lavorazione, compreso il raffreddamento: circa 8-10 min.
Fasi di sonicazione
- Trasferire il lisato in una provetta adatta alla sonicazione. Utilizzare una provetta stretta e a parete sottile che consenta un buon scambio di calore e un'immersione sicura della sonda.
- Mettere la provetta in un bagno di ghiaccio. Il documento indica che il raffreddamento durante la sonicazione è fondamentale per evitare danni da calore.
- Immergere la punta della sonda nel campione. Mantenere la punta sufficientemente immersa per garantire una cavitazione stabile, ma non farla toccare la parete o il fondo della provetta.
- Eseguire un impulso di 5 s all'ampiezza iniziale.
- Riportare immediatamente il campione in ghiaccio per 2 minuti.
- Ripetere fino a completare 4 cicli.
- Ispezionare il lisato dopo il ciclo.
- Continuare solo se necessario, utilizzando un ulteriore impulso di 5 s alla volta, sempre seguito da un raffreddamento completo.
- Interrompere quando il lisato diventa più uniforme e meno filante/vischioso.
Il risultato finale è un lisato più traslucido che forma gocce piuttosto che un flusso viscoso continuo. - Centrifugare a circa 16.000g per 15 minuti a 4°C.
- Trasferire il surnatante chiarificato in una nuova provetta e misurare la concentrazione proteica.
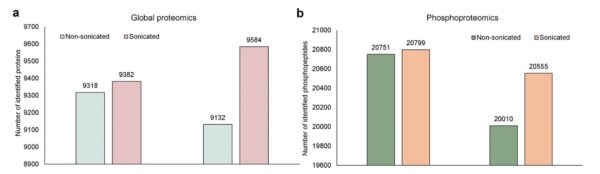
Confronto della proteomica globale e della fosfoproteomica tra campioni sonicati e non sonicati.
a. Numero di proteine identificate (proteomica globale) in tutti i tessuti tumorali PDX con o senza sonicazione. b. Numero di fosfopeptidi identificati (arricchimento IMAC) in tutti i tessuti tumorali PDX con o senza sonicazione. Sono state contate solo le proteine e i fosfopeptidi con un rapporto di abbondanza maggiore o uguale al 25° percentile. Il rapporto di abbondanza è stato calcolato tra gli stessi tipi di campioni.
Studio e grafici: ©Li et al., 2025
Digestione e analisi a valle
Dopo la sonicazione e la chiarificazione, procedere come descritto nel flusso di lavoro originale in stile CPTAC:
- Diluire il lisato 1:3 (v/v) con 50 mM Tris-HCl pH 8.0 per ridurre l'urea a <2 M.
- Aggiungere LysC a 1 mAU per 50 µg di proteina e incubare 2 ore a 25°C.
- Aggiungere tripsina a 1:49 enzima:substrato (p/p) e digerire per una notte a 25°C.
- Raffreddare con acido formico all'1% finale.
- Proseguire con il desalaggio, l'etichettatura TMT, il frazionamento, l'arricchimento dei fosfopeptidi e la LC-MS/MS come richiesto.
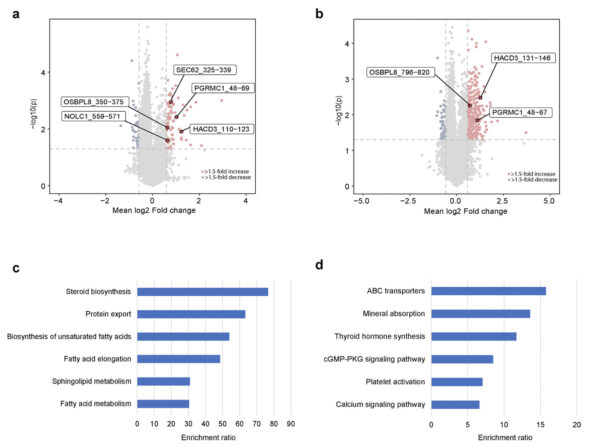
Espressione differenziale di fosfopeptidi da MS marcati con TMT.
a. Il sottotipo basale, evidenziando alcuni fosfopeptidi umani (inizio e fine della sequenza proteica) upregolati nei campioni sonicati rispetto ai campioni non sonicati. b. Il sottotipo luminale, evidenziando alcuni fosfopeptidi umani (inizio e fine della sequenza proteica) upregolati nei campioni sonicati rispetto ai campioni non sonicati. c. Percorsi KEGG arricchiti in base alle proteine dei fosfopeptidi upregolati nel sottotipo basale di tumori sonicati. d. Percorsi KEGG arricchiti in base alle proteine dei fosfopeptidi upregolati nel sottotipo luminale di tumori sonicati.
Studio e grafici: ©Li et al., 2025
Progettazione, produzione e consulenza – Qualità Made in Germany
Gli ultrasuoni Hielscher sono noti per i loro elevati standard di qualità e design. La robustezza e la facilità d'uso consentono un'agevole integrazione dei nostri ultrasuoni negli impianti industriali. Gli ultrasuonatori Hielscher sono in grado di gestire facilmente condizioni difficili e ambienti impegnativi.
Hielscher Ultrasonics è un'azienda certificata ISO e pone particolare enfasi sugli ultrasuonatori ad alte prestazioni, caratterizzati da tecnologia all'avanguardia e facilità d'uso. Naturalmente, gli ultrasuoni Hielscher sono conformi alla normativa CE e soddisfano i requisiti UL, CSA e RoH.

Sonicatore per piastre multipozzetto UIP400MTP per l'estrazione di proteine ad alto rendimento dai campioni
Letteratura / Riferimenti
- Li Q.K.; Lih T.M.; Clark D.J.; Chen L.; Schnaubelt M.; Zhang H. (2025): Sonication-assisted protein extraction improves proteomic detection of membrane-bound and DNA-binding proteins from tumor tissues. Nature Protocols 2025 Aug;20(8):2083-2099.
- Stadlmann, J., Taubenschmid, J., Wenzel, D. et al. (2017): Comparative glycoproteomics of stem cells identifies new players in ricin toxicity. Nature 549, 2017. 538–542
- Jakob, S., Steinchen, W., Hanßmann, J. et al. (2024): The virulence regulator VirB from Shigella flexneri uses a CTP-dependent switch mechanism to activate gene expression. Nature Communications 15, 318 (2024).
- Jorge S., Capelo J.L., LaFramboise W., Dhir R., Lodeiro C., Santos H.M. (2019): Development of a Robust Ultrasonic-Based Sample Treatment To Unravel the Proteome of OCT-Embedded Solid Tumor Biopsies. Journal of Proteome Research 2019 Jul 5;18(7):2979-2986.
- Mertins P, Tang LC, Krug K, et al. (2018): Reproducible workflow for multiplexed deep-scale proteome and phosphoproteome analysis of tumor tissues by liquid chromatography-mass spectrometry. (Initial CPTAC protocol). Nature Protocols 7, 2018. 1632-1661.
Domande frequenti
Qual è la differenza tra l'estrazione di proteine da tessuti vegetali e tessuti di mammiferi?
L'estrazione di proteine dai tessuti vegetali è solitamente più difficile rispetto a quella dei tessuti di mammifero, perché le cellule vegetali hanno una parete cellulare rigida e ricca di cellulosa, abbondanti polisaccaridi, composti fenolici, pigmenti ed enzimi endogeni attivi che possono interferire con la solubilizzazione delle proteine, contaminare gli estratti o promuovere la degradazione delle proteine. Al contrario, il tessuto dei mammiferi non ha una parete cellulare ed è generalmente più facile da disgregare chimicamente, anche se spesso contiene più lipidi, matrice extracellulare e proteasi che possono complicare l'estrazione. Di conseguenza, i protocolli per le piante richiedono in genere una maggiore disgregazione meccanica, una macinazione a bassa temperatura e additivi come PVPP, agenti riducenti o detergenti a base di fenoli, mentre i tessuti di mammifero sono più spesso gestiti con successo con tamponi a base di detergenti come RIPA o sistemi di lisi a base di urea. Entrambi i tessuti, vegetale e di mammifero, possono essere lisati efficacemente mediante sonicazione!
Come migliorare l'estrazione delle proteine dai tessuti utilizzando il tampone RIPA?
L'estrazione di proteine dai tessuti con il tampone RIPA può essere migliorata ottimizzando sia la disgregazione che la protezione del campione. Le misure più importanti sono mantenere il tessuto e il tampone freddi, utilizzare inibitori di proteasi e fosfatasi preparati di recente, tritare o polverizzare accuratamente il tessuto prima della lisi, mantenere un rapporto adeguato tra tampone e tessuto e aggiungere una fase di disgregazione meccanica come l'omogeneizzazione o una breve sonicazione con sonda per rompere il tessuto denso e ridurre la viscosità. L'efficienza dell'estrazione migliora anche quando i lisati vengono incubati in ghiaccio con miscelazione intermittente, seguita da centrifugazione refrigerata ad alta velocità per rimuovere i detriti insolubili. Per i tessuti fibrosi, ricchi di lipidi o altamente strutturati, ripetere l'estrazione una volta o aumentare il tempo di esposizione al detergente può migliorare il recupero, ma occorre evitare una sonicazione eccessiva o una manipolazione prolungata a temperatura ambiente perché possono denaturare le proteine o aumentare la proteolisi.
Quali sono i requisiti di sicurezza da rispettare durante l'estrazione delle proteine a ultrasuoni?
Eseguire la sonicazione della sonda in un box di protezione acustica o con un'adeguata protezione dell'udito. Il protocollo della sorgente avverte specificamente dei rumori acustici nocivi generati durante la sonicazione.
Indossare protezioni per gli occhi, camice e guanti.
Tenere la sonda lontana dalla pelle e non sonicare mai un recipiente aperto senza protezione dagli spruzzi.
Maneggiare il PMSF e gli altri inibitori secondo le norme di sicurezza chimica locali.
Mantenere i campioni in ghiaccio per ridurre il danno proteico indotto dal calore; il documento identifica ripetutamente il controllo della temperatura come critico.

Il Sonicator VialTweeter accelera e migliora l'estrazione delle proteine in proteomica

Hielscher Ultrasonics produce omogeneizzatori a ultrasuoni ad alte prestazioni da laboratorio a dimensioni industriali.


