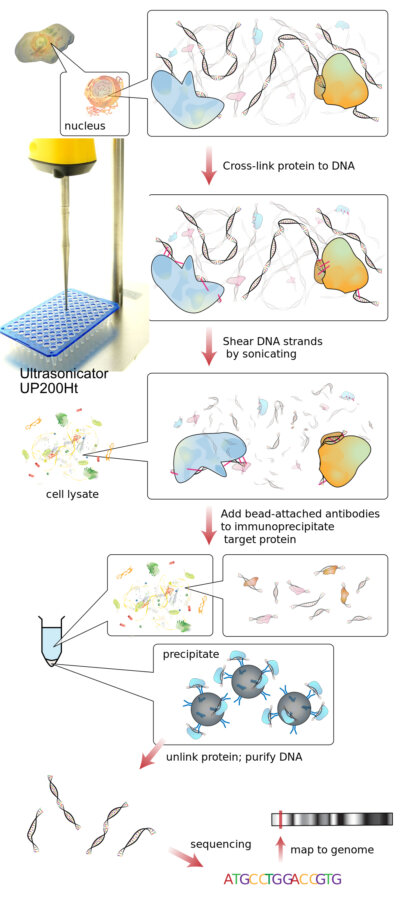
Taglio della cromatina con la sonicazione
Il taglio della cromatina è una fase critica in molti flussi di lavoro di epigenetica e biologia molecolare, in particolare nell'immunoprecipitazione della cromatina (ChIP), nel ChIP-seq e nelle analisi correlate. L'obiettivo è frammentare la cromatina in complessi DNA-proteina riproducibili, preservando l'integrità degli epitopi e riducendo al minimo la perdita di campioni. Tra i metodi disponibili, la frammentazione della cromatina con ultrasuoni è diventata un approccio ampiamente utilizzato perché fornisce una frammentazione affidabile, senza reagenti e con un'eccellente riproducibilità.
Che cosa si deve considerare quando si esegue il taglio della cromatina?
Una frammentazione efficiente della cromatina richiede un attento controllo dei parametri sperimentali. Una frammentazione non corretta può compromettere gli esperimenti ChIP a valle, generando frammenti troppo grandi, eccessivamente degradati o incoerenti tra i campioni.
Uno dei fattori più importanti è la distribuzione delle dimensioni dei frammenti desiderati. Per la maggior parte delle applicazioni ChIP e ChIP-seq, i frammenti di cromatina compresi tra 100 e 600 coppie di basi sono ottimali. Questo intervallo di dimensioni consente un'immunoprecipitazione efficiente, fornendo al contempo una risoluzione sufficiente per la mappatura genomica.
 Un altro fattore chiave è l'efficienza del crosslinking prima della sonicazione. La maggior parte dei flussi di lavoro ChIP prevede la fissazione con formaldeide per stabilizzare le interazioni proteina-DNA. Tuttavia, un'eccessiva reticolazione può rendere la cromatina più resistente alla frammentazione, richiedendo tempi di sonicazione più lunghi e aumentando potenzialmente l'esposizione al calore.
Un altro fattore chiave è l'efficienza del crosslinking prima della sonicazione. La maggior parte dei flussi di lavoro ChIP prevede la fissazione con formaldeide per stabilizzare le interazioni proteina-DNA. Tuttavia, un'eccessiva reticolazione può rendere la cromatina più resistente alla frammentazione, richiedendo tempi di sonicazione più lunghi e aumentando potenzialmente l'esposizione al calore.
Anche il controllo della temperatura è fondamentale. La sonicazione genera energia localizzata che può aumentare la temperatura del campione. Le temperature elevate possono danneggiare il DNA o denaturare le proteine, compromettendo il riconoscimento degli anticorpi durante la ChIP. Per questo motivo, molti ricercatori eseguono cicli di sonicazione pulsata combinati con intervalli di raffreddamento per mantenere la stabilità del campione.
Anche la concentrazione e il volume del campione influenzano l'efficienza della frammentazione. Le sospensioni di cromatina altamente concentrate possono richiedere tempi di sonicazione più lunghi, mentre i piccoli volumi di campione richiedono un'erogazione precisa di energia per evitare una lavorazione eccessiva.
Infine, la scelta del dispositivo di sonicazione influenza fortemente la riproducibilità sperimentale. I dispositivi progettati per il taglio della cromatina forniscono in genere un'energia ultrasonica controllata e una manipolazione standardizzata dei campioni, consentendo una frammentazione coerente su più campioni.
Quale sonicatore scegliere per il taglio della cromatina?
I diversi flussi di lavoro di laboratorio richiedono diverse configurazioni di sonicazione. Il sistema ottimale dipende in larga misura dalla produzione di campioni, dal volume e dal formato sperimentale.
Sonicatore a sonda
Un sonicatore a sonda eroga energia ultrasonica direttamente nel campione attraverso una sonda in titanio. Questa configurazione fornisce una densità di energia molto elevata ed è quindi adatta per una robusta disgregazione della cromatina in campioni individuali.
I sonicatori a sonda sono particolarmente utili per:
- Campioni di piccole e medie dimensioni
- Cromatina difficile da frammentare
- Protocolli sperimentali flessibili
Sonicatore multi-tubo - VialTweeter
Per i laboratori che trattano più campioni contemporaneamente, il sonicatore multi-provetta VialTweeter offre una soluzione altamente riproducibile. Il sistema trasmette l'energia ultrasonica indirettamente attraverso il supporto della fiala, consentendo la frammentazione di più provette sigillate in condizioni identiche.
Questa configurazione offre importanti vantaggi:
- Taglio parallelo della cromatina di più campioni
- Eliminazione della contaminazione della sonda
- Elevata riproducibilità tra le provette
- Flusso di lavoro semplificato per la preparazione dei campioni ChIP
Questi sistemi multi-tubo sono adatti per gli esperimenti ChIP di routine e per gli studi a media produttività.
Sonicatore per micropiastre - UIP400MTP
Gli studi epigenetici ad alta produttività si basano sempre più sull'elaborazione dei campioni su micropiastra. Il sonicatore per micropiastre UIP400MTP è stato progettato per frammentare la cromatina direttamente in micropiastre standard senza trasferire i campioni.
Questo approccio consente di:
- Elaborazione simultanea di decine o centinaia di campioni
- Flussi di lavoro facili da automatizzare
- Distribuzione uniforme dell'energia ultrasonica nei pozzetti
- Riduzione significativa delle fasi di manipolazione dei campioni
Per i grandi progetti di screening ChIP-seq o per gli studi epigenetici ad alto rendimento, la sonicazione delle micropiastre offre una scalabilità e un'efficienza eccezionali. Il sonicatore per piastre multipozzetto UIP400MTP è adatto per integrazione nei sistemi di manipolazione dei liquidi e nei flussi di lavoro automatizzati del laboratorio.
Perché scegliere la sonicazione rispetto ad altre tecniche di taglio della cromatina?
Rispetto agli approcci enzimatici, la sonicazione per la ChIP fornisce una frammentazione imparziale, poiché il processo non dipende dall'attività enzimatica specifica della sequenza. Ciò è particolarmente importante per gli studi epigenetici su tutto il genoma, dove è essenziale una copertura uniforme.
Un altro grande vantaggio è la scalabilità. I sistemi a ultrasuoni possono ospitare campioni singoli, provette multiple o intere micropiastre, consentendo ai laboratori di scegliere la configurazione più adatta alla loro produttività sperimentale.
Infine, la sonicazione offre un eccellente controllo dei parametri di frammentazione. Regolando i cicli di impulsi, la durata e i livelli di potenza, i ricercatori possono ottenere in modo affidabile la distribuzione desiderata delle dimensioni dei frammenti.
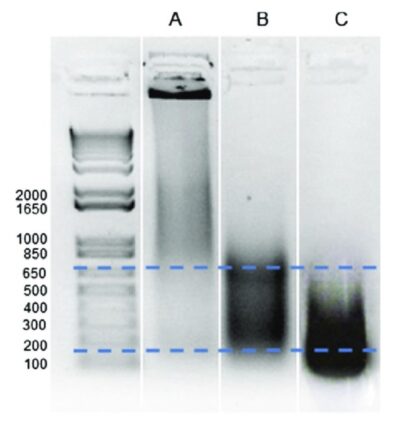
Frammentazione della cromatina mediante sonicazione ottimizzata dei campioni ChIP.
(a) nessun taglio (frammenti lunghi nel gel);
(b) profilo di frammentazione ottimale (arricchimento di frammenti di 200-600 bp);
(c) eccesso di frammentazione del DNA (sovrarappresentazione di frammenti più corti di 200 bp)
© Jarillo et al., 2018
Confronto tra le tecniche di taglio della cromatina
| Metodo di taglio della cromatina | Principio | Vantaggi | Limitazioni |
| Sonicazione | L'energia acustica ad alta frequenza frammenta meccanicamente la cromatina. | Frammentazione senza reagenti, risultati altamente riproducibili, distribuzione delle dimensioni dei frammenti regolabile, compatibilità con la cromatina reticolata, scalabilità da provette singole a formati multi-campione e micropiastra. | Richiede apparecchiature di sonicazione e l'ottimizzazione dei parametri di sonicazione. |
| Digestione enzimatica (MNase) | La nucleasi micrococcica digerisce il DNA tra i nucleosomi. | Frammentazione delicata e utile per l'analisi della cromatina nativa. | Bias enzimatico, preferenza di sequenza, digestione difficile da controllare, potenziale variabilità tra gli esperimenti. |
| Taglio meccanico (ago/siringa) | La cromatina viene disgregata attraverso una forza fisica ripetuta. | Metodo semplice che richiede un'attrezzatura minima. | Scarsa riproducibilità, controllo limitato sulle dimensioni dei frammenti, lavoro intensivo per campioni multipli. |
| Nebulizzazione | L'aria compressa spinge il DNA attraverso piccoli orifizi causandone la frammentazione. | Processo di frammentazione rapido. | Possibile perdita di campioni, scalabilità limitata, richiede apparecchiature specializzate. |
Come quantificare e qualificare la resa della cromatina dopo la frammentazione a ultrasuoni?
 Dopo la sonicazione per la ChIP, i ricercatori devono valutare sia la quantità che la qualità della cromatina frammentata. Questa fase di verifica assicura che la frammentazione della cromatina soddisfi i requisiti delle applicazioni a valle, come la ChIP-qPCR o la ChIP-seq.
Dopo la sonicazione per la ChIP, i ricercatori devono valutare sia la quantità che la qualità della cromatina frammentata. Questa fase di verifica assicura che la frammentazione della cromatina soddisfi i requisiti delle applicazioni a valle, come la ChIP-qPCR o la ChIP-seq.
La quantificazione inizia tipicamente con la misurazione della concentrazione di DNA. Metodi spettrofotometrici come l'analisi Nanodrop o saggi fluorimetrici come la quantificazione del DNA Qubit forniscono stime affidabili della resa della cromatina dopo la decrosslinking e la purificazione.
Tuttavia, la concentrazione di DNA da sola non rivela se la frammentazione è avvenuta con successo. I ricercatori valutano quindi la distribuzione delle dimensioni dei frammenti utilizzando tecniche elettroforetiche. L'elettroforesi su gel di agarosio rimane un approccio comunemente utilizzato per visualizzare i frammenti di DNA e verificare che la maggior parte di essi rientri nell'intervallo di dimensioni previsto.
I laboratori più avanzati utilizzano spesso sistemi di elettroforesi capillare, come il Bioanalyzer o la TapeStation di Agilent. Queste piattaforme forniscono profili precisi di distribuzione dimensionale e consentono ai ricercatori di rilevare un'eccessiva frammentazione o un taglio incompleto.
Quando si valuta la qualità della cromatina dopo la frammentazione a ultrasuoni, i ricercatori confermano in genere:
- La maggior parte dei frammenti di DNA rientra nell'intervallo 100-600 bp.
- La distribuzione dei frammenti è coerente tra i campioni replicati
- La degradazione del DNA è minima
- La resa di cromatina totale è sufficiente per il saggio ChIP previsto.
Un adeguato controllo di qualità assicura che la fase di taglio della cromatina a ultrasuoni produca risultati riproducibili e biologicamente significativi.
Conclusione: Il taglio della cromatina a ultrasuoni per una ricerca affidabile
Il taglio affidabile della cromatina è fondamentale per il successo della ricerca ChIP ed epigenetica. La frammentazione a ultrasuoni offre una soluzione potente perché consente una rottura della cromatina precisa, riproducibile e senza reagenti in un'ampia gamma di formati sperimentali.
Ottimizzando con cura i parametri di sonicazione, verificando la distribuzione delle dimensioni dei frammenti e selezionando il sistema di sonicazione appropriato – sia che si tratti di un sonicatore a sonda, di un VialTweeter multi-tubo o del sonicatore per micropiastre ad alta produttività UIP400MTP – i ricercatori possono ottenere una frammentazione coerente della cromatina che supporta risultati ChIP e ChIP-seq di alta qualità.
Mentre la ricerca epigenetica continua ad espandersi verso una maggiore produttività e una maggiore riproducibilità sperimentale, il taglio della cromatina a ultrasuoni rimane uno dei metodi più versatili e affidabili disponibili per i moderni laboratori di biologia molecolare.
Progettazione, produzione e consulenza – Qualità Made in Germany
Gli ultrasuoni Hielscher sono noti per i loro elevati standard di qualità e design. La robustezza e la facilità d'uso consentono un'agevole integrazione dei nostri ultrasuoni negli impianti industriali. Gli ultrasuonatori Hielscher sono in grado di gestire facilmente condizioni difficili e ambienti impegnativi.
Hielscher Ultrasonics è un'azienda certificata ISO e pone particolare enfasi sugli ultrasuonatori ad alte prestazioni, caratterizzati da tecnologia all'avanguardia e facilità d'uso. Naturalmente, gli ultrasuoni Hielscher sono conformi alla normativa CE e soddisfano i requisiti UL, CSA e RoH.
Letteratura / Riferimenti
- Dreyer J., Ricci G., van den Berg J., Bhardwaj V., Funk J., Armstrong C., van Batenburg V., Sine C., VanInsberghe M.A., Marsman R., Mandemaker I.K., di Sanzo S., Costantini J., Manzo S.G., Biran A., Burny C., Völker-Albert M., Groth A., Spencer S.L., van Oudenaarden A., Mattiroli F. (2024): Acute multi-level response to defective de novo chromatin assembly in S-phase. Molecular Cell 2024.
- Mittal, N., Guimaraes, J.C., Gross, T. et al. (2017): The Gcn4 transcription factor reduces protein synthesis capacity and extends yeast lifespan. Nat Commun 8, 457 (2017).
- Shih H.-T., Chen W.-Y., Liu K.-Y., Shih Z.-S., Chen Y.-J., Hsieh P.-C., et al. (2016): dBRWD3 Regulates Tissue Overgrowth and Ectopic Gene Expression Caused by Polycomb Group Mutations. PLoS Genetics 12(9): e1006262.
- José A. Jarillo, Dorota N. Komar, and Manuel Piñeiro (2018): The Use of the Chromatin Immunoprecipitation Technique for In Vivo Identification of Plant Protein–DNA Interactions. Chapter in book: Luis Oñate-Sánchez (ed.), Two-Hybrid Systems: Methods and Protocols, Methods in Molecular Biology, vol. 1794, 2018.
- Einig, E., Jin, C., Andrioletti, V. et al. (2023): RNAPII-dependent ATM signaling at collisions with replication forks. Nature Communications 14, 5147 (2023)
Domande frequenti
Che cos'è la cromatina?
La cromatina è il complesso strutturale di DNA e proteine associate che organizza il materiale genetico all'interno del nucleo delle cellule eucariotiche. Le proteine principali della cromatina sono gli istoni, attorno ai quali si avvolge il DNA per formare i nucleosomi. Questa organizzazione compatta il DNA e contemporaneamente regola l'accesso alle informazioni genetiche per processi come la trascrizione, la replicazione e la riparazione del DNA.
Quali sono i tipi di cromatina?
La cromatina è generalmente classificata in due forme principali: eucromatina ed eterocromatina. L'eucromatina è poco compatta e attiva dal punto di vista trascrizionale, consentendo ai geni di essere facilmente accessibili al macchinario trascrizionale. L'eterocromatina è più densa e inattiva dal punto di vista trascrizionale e contiene tipicamente sequenze di DNA ripetitive o geni silenziati. L'eterocromatina può essere ulteriormente suddivisa in eterocromatina costitutiva, che rimane permanentemente condensata, ed eterocromatina facoltativa, che può passare dallo stato attivo a quello inattivo a seconda delle condizioni cellulari.
Che cos'è il crosslinking?
La reticolazione è un processo biochimico utilizzato per stabilizzare le interazioni tra biomolecole formando legami covalenti tra di esse. Nella ricerca sulla cromatina, la reticolazione è comunemente utilizzata per preservare le interazioni proteina-DNA all'interno della cromatina prima dell'analisi. Agenti chimici come la formaldeide vengono utilizzati per creare legami covalenti reversibili tra il DNA e le proteine associate. “congelamento” interazioni molecolari in un momento specifico. Questa stabilizzazione permette ai complessi cromatinici di essere frammentati e processati senza perdere le associazioni native tra DNA e proteine regolatrici, il che è essenziale per tecniche come l'immunoprecipitazione della cromatina (ChIP).
Che cos'è la ChIP?
L'immunoprecipitazione della cromatina (ChIP) è una tecnica di biologia molecolare utilizzata per studiare le interazioni tra proteine e DNA all'interno della cromatina. In questo metodo, i complessi DNA-proteina vengono prima stabilizzati, in genere mediante reticolazione, e la cromatina viene poi frammentata. Gli anticorpi specifici per una proteina bersaglio vengono utilizzati per immunoprecipitare i complessi proteina-DNA, consentendo di isolare e analizzare le sequenze di DNA associate.
A cosa serve la ChIP?
La ChIP viene utilizzata per identificare le regioni genomiche legate da specifiche proteine associate al DNA, come i fattori di trascrizione, le modifiche degli istoni o le proteine regolatrici associate alla cromatina. La tecnica è ampiamente applicata per studiare la regolazione genica, le modificazioni epigenetiche, i siti di legame dei fattori di trascrizione e la struttura della cromatina. Se combinata con metodi analitici a valle, come la PCR quantitativa (ChIP-qPCR) o il sequenziamento ad alto rendimento (ChIP-seq), consente di mappare a livello genomico le interazioni proteina-DNA.
Quali sono i tipi di ChIP?
Esistono diverse varianti dell'immunoprecipitazione della cromatina a seconda del disegno sperimentale e dell'analisi a valle. Gli approcci più comuni includono la ChIP-qPCR, che quantifica l'arricchimento di specifiche regioni genomiche; la ChIP-seq, che utilizza il sequenziamento di nuova generazione per mappare le interazioni proteina-DNA in tutto il genoma; e la ChIP-chip, che combina la ChIP con l'analisi del DNA microarray. A seconda del quesito biologico da indagare, sono ampiamente utilizzate anche altre varianti, come la ChIP nativa (N-ChIP), che analizza la cromatina non reticolata, e la ChIP reticolata (X-ChIP), che utilizza un reticolo chimico per stabilizzare le interazioni proteina-DNA.

Hielscher Ultrasonics produce omogeneizzatori a ultrasuoni ad alte prestazioni da laboratorio a dimensioni industriali.