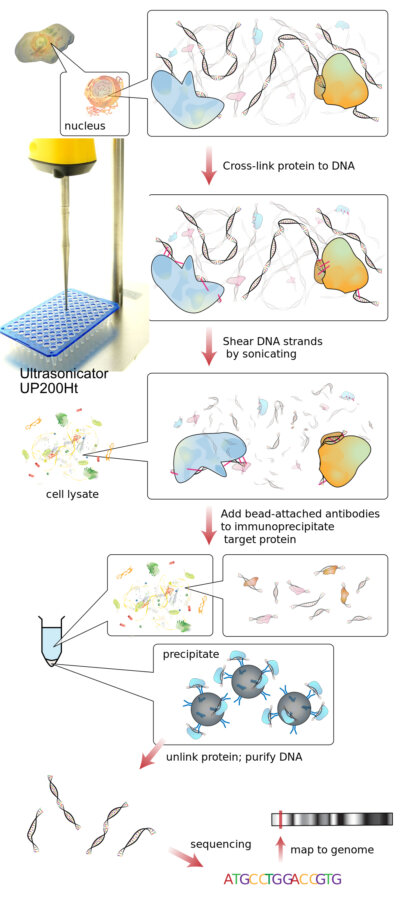
Ścinanie chromatyny za pomocą sonikacji
Ścinanie chromatyny jest krytycznym krokiem w wielu procesach epigenetyki i biologii molekularnej, szczególnie w immunoprecypitacji chromatyny (ChIP), ChIP-seq i powiązanych testach. Celem jest fragmentacja chromatyny w powtarzalne kompleksy DNA-białko przy jednoczesnym zachowaniu integralności epitopu i zminimalizowaniu utraty próbki. Spośród dostępnych metod, ultradźwiękowa fragmentacja chromatyny stała się szeroko stosowanym podejściem, ponieważ zapewnia niezawodną, wolną od odczynników fragmentację o doskonałej powtarzalności.
Co należy wziąć pod uwagę podczas ścinania chromatyny?
Skuteczne ścinanie chromatyny wymaga starannej kontroli parametrów eksperymentalnych. Niewłaściwa fragmentacja może zagrozić dalszym eksperymentom ChIP poprzez generowanie fragmentów, które są zbyt duże, nadmiernie zdegradowane lub niespójne między próbkami.
Jednym z najważniejszych czynników jest pożądany rozkład wielkości fragmentów. Dla większości zastosowań ChIP i ChIP-seq optymalne są fragmenty chromatyny o wielkości od 100 do 600 par zasad. Ten zakres wielkości umożliwia wydajną immunoprecypitację, zapewniając jednocześnie wystarczającą rozdzielczość do mapowania genomu.
 Innym kluczowym czynnikiem jest skuteczność sieciowania przed sonikacją. Większość przepływów pracy ChIP obejmuje utrwalanie formaldehydem w celu stabilizacji interakcji białko-DNA. Jednak nadmierne sieciowanie może sprawić, że chromatyna będzie bardziej odporna na fragmentację, wymagając dłuższych czasów sonikacji i potencjalnie zwiększając ekspozycję na ciepło.
Innym kluczowym czynnikiem jest skuteczność sieciowania przed sonikacją. Większość przepływów pracy ChIP obejmuje utrwalanie formaldehydem w celu stabilizacji interakcji białko-DNA. Jednak nadmierne sieciowanie może sprawić, że chromatyna będzie bardziej odporna na fragmentację, wymagając dłuższych czasów sonikacji i potencjalnie zwiększając ekspozycję na ciepło.
Kluczowe znaczenie ma również kontrola temperatury. Sonikacja generuje zlokalizowaną energię, która może podnieść temperaturę próbki. Podwyższona temperatura może uszkodzić DNA lub denaturować białka, wpływając na rozpoznawanie przeciwciał podczas ChIP. Dlatego wielu badaczy wykonuje pulsacyjne cykle sonikacji w połączeniu z przerwami na chłodzenie, aby utrzymać stabilność próbki.
Stężenie i objętość próbki również wpływają na wydajność fragmentacji. Wysoce skoncentrowane zawiesiny chromatyny mogą wymagać dłuższych czasów sonikacji, podczas gdy małe objętości próbek wymagają precyzyjnego dostarczania energii, aby zapobiec nadmiernemu przetwarzaniu.
Wreszcie, wybór urządzenia do sonikacji silnie wpływa na powtarzalność eksperymentalną. Urządzenia zaprojektowane do ścinania chromatyny zazwyczaj zapewniają kontrolowaną energię ultradźwiękową i znormalizowaną obsługę próbek, umożliwiając spójną fragmentację wielu próbek.
Który sonikator wybrać do ścinania chromatyny?
Różne przepływy pracy w laboratorium wymagają różnych konfiguracji sonikacji. Optymalny system zależy w dużej mierze od przepustowości próbki, objętości i formatu eksperymentalnego.
Sonikator typu sonda
Sonikator typu sondowego dostarcza energię ultradźwiękową bezpośrednio do próbki poprzez tytanową sondę. Ta konfiguracja zapewnia bardzo wysoką gęstość energii i dlatego jest odpowiednia do solidnego rozbijania chromatyny w poszczególnych próbkach.
Sonikatory są szczególnie przydatne do:
- Liczba próbek od małej do średniej
- Chromatyna trudna do fragmentacji
- Elastyczne protokoły eksperymentalne
Sonikator wielotubowy - VialTweeter
Dla laboratoriów przetwarzających wiele próbek jednocześnie, sonikator wielopróbkowy VialTweeter zapewnia wysoce powtarzalne rozwiązanie. System przesyła energię ultradźwiękową pośrednio przez uchwyt fiolki, umożliwiając fragmentację kilku zamkniętych probówek w identycznych warunkach.
Taka konfiguracja oferuje istotne korzyści:
- Równoległe ścinanie chromatyny wielu próbek
- Eliminacja zanieczyszczenia sondy
- Wysoka powtarzalność pomiędzy tubami
- Uproszczony proces przygotowania próbek ChIP
Takie systemy wielorurkowe dobrze nadają się do rutynowych eksperymentów ChIP i badań o średniej przepustowości.
Sonikator mikropłytek - UIP400MTP
Wysokowydajne badania epigenetyczne w coraz większym stopniu opierają się na przetwarzaniu próbek na mikropłytkach. Sonikator mikropłytek UIP400MTP został zaprojektowany do fragmentacji chromatyny bezpośrednio w standardowych mikropłytkach bez konieczności przenoszenia próbek.
Takie podejście umożliwia:
- Jednoczesne przetwarzanie dziesiątek lub setek próbek
- Przepływy pracy przyjazne dla automatyzacji
- Równomierny rozkład energii ultradźwiękowej w studniach
- Znaczna redukcja etapów obsługi próbek
W przypadku dużych projektów przesiewowych ChIP-seq lub wysokoprzepustowych badań epigenetycznych, sonikacja mikropłytek zapewnia wyjątkową skalowalność i wydajność. Sonikator wielodołkowy UIP400MTP doskonale nadaje się do integracja z systemami obsługi cieczy i zautomatyzowanymi procesami laboratoryjnymi.
Dlaczego warto wybrać sonikację zamiast innych technik ścinania chromatyny?
W porównaniu z metodami enzymatycznymi, sonikacja dla ChIP zapewnia bezstronną fragmentację, ponieważ proces ten nie zależy od aktywności enzymu specyficznego dla sekwencji. Jest to szczególnie ważne w badaniach epigenetycznych obejmujących cały genom, gdzie niezbędne jest jednolite pokrycie.
Kolejną ważną zaletą jest skalowalność. Systemy ultradźwiękowe mogą pomieścić pojedyncze próbki, wiele probówek lub całe mikropłytki, umożliwiając laboratoriom wybór najbardziej odpowiedniej konfiguracji dla ich przepustowości eksperymentalnej.
Wreszcie, sonikacja zapewnia doskonałą kontrolę nad parametrami fragmentacji. Dostosowując cykle impulsów, czas trwania i poziomy mocy, naukowcy mogą niezawodnie osiągnąć pożądany rozkład wielkości fragmentów.
Porównanie technik ścinania chromatyny
| Metoda ścinania chromatyny | Zasada | Zalety | Ograniczenia |
| sonikacja | Energia akustyczna o wysokiej częstotliwości mechanicznie fragmentuje chromatynę. | Fragmentacja bez użycia odczynników, wysoce powtarzalne wyniki, przestrajalny rozkład wielkości fragmentów, kompatybilność z usieciowaną chromatyną, skalowalność od pojedynczych probówek do wielu próbek i formatów mikropłytek. | Wymaga sprzętu do sonikacji i optymalizacji parametrów sonikacji. |
| Trawienie enzymatyczne (MNaza) | Nukleaza mikrokokowa trawi DNA pomiędzy nukleosomami. | Delikatna fragmentacja, przydatna do analizy natywnej chromatyny. | Stronniczość enzymu, preferencja sekwencji, trawienie trudne do kontrolowania, potencjalna zmienność między eksperymentami. |
| Mechaniczne ścinanie (igła/strzykawka) | Chromatyna jest zakłócana przez powtarzającą się siłę fizyczną. | Prosta metoda wymagająca minimalnej ilości sprzętu. | Słaba powtarzalność, ograniczona kontrola nad wielkością fragmentów, pracochłonność w przypadku wielu próbek. |
| Nebulizacja | Sprężone powietrze przeciska DNA przez małe otwory, powodując fragmentację. | Szybki proces fragmentacji. | Możliwa utrata próbki, ograniczona skalowalność, wymaga specjalistycznego sprzętu. |
Jak określić ilościowo i jakościowo wydajność chromatyny po fragmentacji ultradźwiękowej?
 Po sonikacji do ChIP, badacze muszą ocenić zarówno ilość, jak i jakość pofragmentowanej chromatyny. Ten etap weryfikacji zapewnia, że fragmentacja chromatyny spełnia wymagania dalszych zastosowań, takich jak ChIP-qPCR lub ChIP-seq.
Po sonikacji do ChIP, badacze muszą ocenić zarówno ilość, jak i jakość pofragmentowanej chromatyny. Ten etap weryfikacji zapewnia, że fragmentacja chromatyny spełnia wymagania dalszych zastosowań, takich jak ChIP-qPCR lub ChIP-seq.
Kwantyfikacja zazwyczaj rozpoczyna się od pomiaru stężenia DNA. Metody spektrofotometryczne, takie jak analiza Nanodrop lub testy fluorometryczne, takie jak kwantyfikacja DNA Qubit, zapewniają wiarygodne szacunki wydajności chromatyny po usieciowaniu i oczyszczeniu.
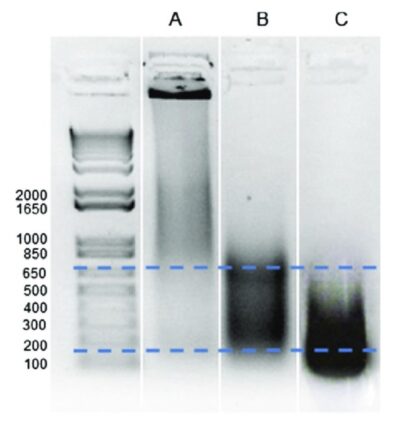
Jednak samo stężenie DNA nie ujawnia, czy fragmentacja zakończyła się sukcesem. Badacze oceniają zatem rozkład wielkości fragmentów przy użyciu technik elektroforetycznych. Elektroforeza w żelu agarozowym pozostaje powszechnie stosowanym podejściem do wizualizacji fragmentów DNA i weryfikacji, czy większość mieści się w docelowym zakresie wielkości.
Bardziej zaawansowane laboratoria często korzystają z systemów elektroforezy kapilarnej, takich jak Agilent Bioanalyzer lub TapeStation. Platformy te zapewniają precyzyjne profile rozkładu wielkości i pozwalają badaczom wykryć nadmierną fragmentację lub niepełne ścinanie.
Oceniając jakość chromatyny po fragmentacji ultradźwiękowej, badacze zazwyczaj potwierdzają:
- Większość fragmentów DNA mieści się w zakresie 100-600 bp
- Rozkład fragmentów jest spójny w replikowanych próbkach
- Degradacja DNA jest minimalna
- Całkowita wydajność chromatyny jest wystarczająca dla planowanego testu ChIP
Właściwa kontrola jakości zapewnia, że etap ultradźwiękowego ścinania chromatyny daje powtarzalne i biologicznie znaczące wyniki.
Wnioski: Ultradźwiękowe ścinanie chromatyny dla wiarygodnych badań
Niezawodne ścinanie chromatyny ma fundamentalne znaczenie dla udanych badań ChIP i epigenetyki. Fragmentacja ultradźwiękowa oferuje potężne rozwiązanie, ponieważ umożliwia precyzyjne, powtarzalne i wolne od odczynników rozerwanie chromatyny w szerokim zakresie formatów eksperymentalnych.
Poprzez staranną optymalizację parametrów sonikacji, weryfikację rozkładu wielkości fragmentów i wybór odpowiedniego systemu sonikacji – sonikator typu sonda, wielorurowy sonikator VialTweeter lub wysokowydajny sonikator do mikropłytek UIP400MTP – Naukowcy mogą osiągnąć spójną fragmentację chromatyny, która wspiera wysokiej jakości wyniki ChIP i ChIP-seq.
Ponieważ badania nad epigenetyką nadal rozwijają się w kierunku większej wydajności i większej powtarzalności eksperymentalnej, ultradźwiękowe ścinanie chromatyny pozostaje jedną z najbardziej wszechstronnych i niezawodnych metod dostępnych dla nowoczesnych laboratoriów biologii molekularnej.
Projektowanie, produkcja i doradztwo – Jakość Made in Germany
Ultradźwięki Hielscher są dobrze znane z najwyższej jakości i standardów projektowych. Solidność i łatwa obsługa pozwalają na płynną integrację naszych ultradźwiękowców z obiektami przemysłowymi. Trudne warunki i wymagające środowiska są łatwo obsługiwane przez ultradźwięki Hielscher.
Hielscher Ultrasonics jest firmą posiadającą certyfikat ISO i kładzie szczególny nacisk na wysokowydajne ultradźwięki z najnowocześniejszą technologią i łatwością obsługi. Oczywiście ultradźwięki Hielscher są zgodne z CE i spełniają wymagania UL, CSA i RoHs.
Literatura / Referencje
- Dreyer J., Ricci G., van den Berg J., Bhardwaj V., Funk J., Armstrong C., van Batenburg V., Sine C., VanInsberghe M.A., Marsman R., Mandemaker I.K., di Sanzo S., Costantini J., Manzo S.G., Biran A., Burny C., Völker-Albert M., Groth A., Spencer S.L., van Oudenaarden A., Mattiroli F. (2024): Acute multi-level response to defective de novo chromatin assembly in S-phase. Molecular Cell 2024.
- Mittal, N., Guimaraes, J.C., Gross, T. et al. (2017): The Gcn4 transcription factor reduces protein synthesis capacity and extends yeast lifespan. Nat Commun 8, 457 (2017).
- Shih H.-T., Chen W.-Y., Liu K.-Y., Shih Z.-S., Chen Y.-J., Hsieh P.-C., et al. (2016): dBRWD3 Regulates Tissue Overgrowth and Ectopic Gene Expression Caused by Polycomb Group Mutations. PLoS Genetics 12(9): e1006262.
- José A. Jarillo, Dorota N. Komar, and Manuel Piñeiro (2018): The Use of the Chromatin Immunoprecipitation Technique for In Vivo Identification of Plant Protein–DNA Interactions. Chapter in book: Luis Oñate-Sánchez (ed.), Two-Hybrid Systems: Methods and Protocols, Methods in Molecular Biology, vol. 1794, 2018.
- Einig, E., Jin, C., Andrioletti, V. et al. (2023): RNAPII-dependent ATM signaling at collisions with replication forks. Nature Communications 14, 5147 (2023)
często zadawane pytania
Czym jest chromatyna?
Chromatyna to strukturalny kompleks DNA i powiązanych z nim białek, który organizuje materiał genetyczny w jądrze komórek eukariotycznych. Podstawowymi białkami w chromatynie są histony, wokół których DNA jest owinięte, tworząc nukleosomy. Ta organizacja zagęszcza DNA, jednocześnie regulując dostęp do informacji genetycznej w procesach takich jak transkrypcja, replikacja i naprawa DNA.
Jakie są rodzaje chromatyny?
Chromatyna jest ogólnie podzielona na dwie główne formy: euchromatynę i heterochromatynę. Euchromatyna jest luźno upakowana i aktywna transkrypcyjnie, umożliwiając łatwy dostęp do genów przez maszynerię transkrypcyjną. Heterochromatyna jest gęściej upakowana i nieaktywna transkrypcyjnie, zazwyczaj zawiera powtarzające się sekwencje DNA lub geny, które są wyciszone. Heterochromatynę można dalej podzielić na heterochromatynę konstytutywną, która pozostaje trwale skondensowana, oraz heterochromatynę fakultatywną, która może przełączać się między stanem aktywnym i nieaktywnym w zależności od warunków komórkowych.
Co to jest Crosslinking?
Sieciowanie to proces biochemiczny stosowany do stabilizacji interakcji między biomolekułami poprzez tworzenie między nimi wiązań kowalencyjnych. W badaniach chromatyny, sieciowanie jest powszechnie stosowane w celu zachowania interakcji białko-DNA w chromatynie przed analizą. Czynniki chemiczne, takie jak formaldehyd, są zwykle stosowane do tworzenia odwracalnych wiązań kowalencyjnych między DNA i powiązanymi białkami, skutecznie “zamrażanie” interakcji molekularnych w określonym momencie. Stabilizacja ta pozwala na fragmentację i przetwarzanie kompleksów chromatynowych bez utraty natywnych powiązań między DNA i białkami regulatorowymi, co jest niezbędne w technikach takich jak immunoprecypitacja chromatyny (ChIP).
Co to jest ChIP?
Immunoprecypitacja chromatyny (ChIP) to technika biologii molekularnej stosowana do badania interakcji między białkami i DNA w chromatynie. W metodzie tej kompleksy DNA-białko są najpierw stabilizowane, zazwyczaj poprzez sieciowanie, a następnie chromatyna jest fragmentowana. Przeciwciała specyficzne dla białka docelowego są używane do immunoprecypitacji kompleksów białko-DNA, umożliwiając izolację i analizę powiązanych sekwencji DNA.
Do czego służy ChIP?
ChIP służy do identyfikacji regionów genomu związanych przez określone białka związane z DNA, takie jak czynniki transkrypcyjne, modyfikacje histonów lub białka regulatorowe związane z chromatyną. Technika ta jest szeroko stosowana do badania regulacji genów, modyfikacji epigenetycznych, miejsc wiązania czynników transkrypcyjnych i struktury chromatyny. W połączeniu z dalszymi metodami analitycznymi, takimi jak ilościowy PCR (ChIP-qPCR) lub sekwencjonowanie o wysokiej przepustowości (ChIP-seq), umożliwia mapowanie interakcji białko-DNA w całym genomie.
Jakie są rodzaje ChIP?
Istnieje kilka wariantów immunoprecypitacji chromatyny w zależności od projektu eksperymentalnego i dalszej analizy. Najpopularniejsze podejścia obejmują ChIP-qPCR, który określa ilościowo wzbogacenie określonych regionów genomu; ChIP-seq, który wykorzystuje sekwencjonowanie nowej generacji do mapowania interakcji białko-DNA w całym genomie; oraz ChIP-chip, który łączy ChIP z analizą mikromacierzy DNA. Dodatkowe warianty, takie jak natywny ChIP (N-ChIP), który analizuje nieusieciowaną chromatynę, oraz usieciowany ChIP (X-ChIP), który wykorzystuje sieciowanie chemiczne do stabilizacji interakcji białko-DNA, są również szeroko stosowane w zależności od badanego zagadnienia biologicznego.

Hielscher Ultrasonics produkuje wysokowydajne homogenizatory ultradźwiękowe od laboratorium do rozmiar przemysłowy.